MOF书籍示例第一章(基础)
本章为MOF简介基础章节,显示可以使用的基础功能和排版
第一章:MOF 基础概念与结构¶
1.1 什么是 MOF?¶
金属有机骨架(Metal–Organic Framework, MOF)是一类由金属节点和有机配体组成的多孔晶体材料。
金属节点:通常是金属离子或金属簇(如 Zn²⁺, Cu²⁺, Zr⁴⁺ 等)
有机配体:含羧酸、吡啶等配位基团的多齿配体
特点:比表面积超大、结构可设计、官能化灵活
MOF 材料最大的特点是其超高的比表面积和可调控的孔径结构。你可以把它们想象成纳米级别的乐高积木。
如文献 Yaghi, 2025 所示[1]
1.2 典型结构示意与晶胞¶
1.2.1 结构示意图片¶
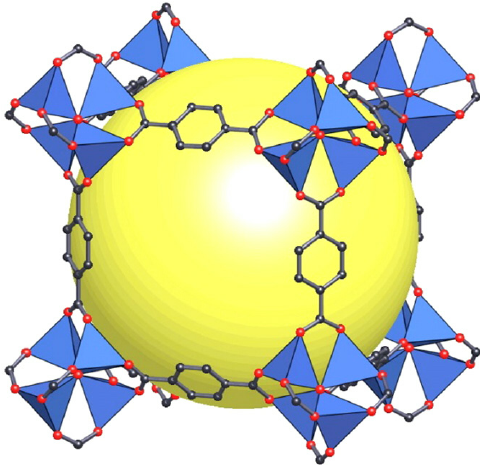
Figure 1:一个 MOF 结构示意图。
1.3 简单晶体学表达¶
下面使用公式描述简单的 MOF 框架晶胞尺寸及孔隙率。
1.3.1 体积与孔隙率¶
晶胞体积:
假设以分子模拟或吸附实验得到 MOF 的空隙体积 ,则孔隙率 可写为:
1.4 表格:一些常见 MOF¶
| 名称 | 金属中心 | 有机配体 | 特点 |
|---|---|---|---|
| MOF-5 | Zn²⁺ | 1,4-苯二甲酸 (BDC) | 早期经典 MOF, 高比表面积 |
| UiO-66 | Zr⁴⁺ | BDC | 热/化学稳定性好 |
| HKUST-1 | Cu²⁺ | 1,3,5-苯三甲酸 (BTC) | 经典铜基 MOF |
| MIL-101(Cr) | Cr³⁺ | BDC | 超大孔体积, 良好水稳定性 |
1.5 使用python代码描述MOF¶
def describe_mof(name, metal, linker):
return f"{name} is a MOF with {metal} as the metal center and {linker} as the organic linker."
print(describe_mof("UiO-66", "Zr⁴⁺", "BDC"))上面是python coding的MOF描述代码,describe_mof。
1.6 使用python代码计算孔隙率与孔体积关系¶
Source
import math
def pore_volume(cube_length_nm, void_fraction):
"""
Simple cubic model.
cube_length_nm: cell edge length (nm)
void_fraction: porosity (void fraction)
Returns pore volume (nm^3)
"""
v_cell = cube_length_nm**3
return v_cell * void_fraction
for phi in [0.3, 0.5, 0.8]:
print(f"Porosity {phi:.1f} -> Pore volume: {pore_volume(2.5, phi):.2f} nm^3")1.7 简单 2D 图示例¶
import numpy as np
import matplotlib.pyplot as plt
phis = np.linspace(0.1, 0.9, 9)
surface_area = 1500 * phis * 2 # Hypothetical relation
plt.figure()
plt.plot(phis, surface_area, marker="o")
plt.xlabel("Porosity φ")
plt.ylabel("Surface Area (m²/g)")
plt.title("Simple Relationship Between Porosity and Surface Area")
plt.grid(True)
plt.show()1.8 交互式MOF结构¶
1.8 An interactive MOF structure¶
Source
from ase.io import read
from ase.visualize import view
# Read structure from a local file, e.g. CIF/PDB
mof_from_file = read("../data/MOF-5.pdb")
# View the periodic structure
disp_mof=view(mof_from_file, viewer='x3d')
display(disp_mof)1.9 练习区(task list)¶
This is a review about AI for MOFs.
- Zheng, Z., Rampal, N., Inizan, T. J., Borgs, C., Chayes, J. T., & Yaghi, O. M. (2025). Large language models for reticular chemistry. Nature Reviews Materials, 10(5), 369–381. 10.1038/s41578-025-00772-8